Krzywe PES dysocjacji z Qunova HiVQE
Funkcje Qiskit to funkcja eksperymentalna dostępna wyłącznie dla użytkowników planów IBM Quantum® Premium Plan, Flex Plan oraz On-Prem (przez IBM Quantum Platform API). Są one w fazie podglądu i mogą ulec zmianie.
Szacunkowe zużycie zasobów (UWAGA: to tylko szacunek. Rzeczywisty czas wykonania może się różnić.)
- Li2S: Pięć minut czasu QPU na procesorze Heron r2
- FeP-NO: Pięć minut czasu QPU na procesorze Heron r2
Wprowadzenie
Dokładne obliczanie energii reakcji chemicznych ma kluczowe znaczenie dla postępu naukowego w dziedzinie materiałoznawstwa, inżynierii chemicznej, odkrywania leków i innych dziedzin. Wśród różnych układów chemicznych szczególnym zainteresowaniem cieszy się układ Li-S, istotny dla zrozumienia i opracowania nowych składów baterii. Ten samouczek umożliwia zdobycie praktycznego doświadczenia w obliczaniu potencjalnej powierzchni energii (PES) dysocjacji wiązania Li-S w układzie poprzez usunięcie jednego atomu litu przy użyciu obliczeń HiVQE. Wyniki można porównać z obliczeniami referencyjnymi (CASCI) oraz klasycznymi metodami, takimi jak Hartree-Fock (HF), dla problemu 20-qubitowego.
Wymagania
Zainstaluj następujące zależności, aby uruchomić kod z tego samouczka.
!pip install --upgrade pip
!pip install -U qiskit-ibm-catalog "qiskit_ibm_runtime<0.42.0" pyscf numpy matplotlib typing_extensions
Konfiguracja
Aby uruchomić ten samouczek, zaimportuj funkcję qunova/hivqe-chemistry przez QiskitFunctionCatalog. Do uruchomienia tej funkcji potrzebujesz konta IBM Quantum Premium Plan, Flex Plan lub On-Prem (IBM Quantum Platform API) Plan oraz licencji od Qunova.
from qiskit_ibm_catalog import QiskitFunctionsCatalog
from pyscf import gto, scf, mcscf
import matplotlib.pyplot as plt
import pprint
catalog = QiskitFunctionsCatalog(
channel="ibm_quantum_platform",
instance="INSTANCE_CRN",
token="YOUR_API_KEY", # Use the 44-character API_KEY you created and saved from the IBM Quantum Platform Home dashboard
)
hivqe = catalog.load("qunova/hivqe-chemistry")
Część 1: Li2S (20Q)
Krok 1: Odwzorowanie klasycznych danych wejściowych na problem kwantowy
Zdefiniuj geometrie w formacie słownikowym dla różnych odległości wiązania Li-S, aby obliczyć krzywą PES. Geometrie te są zoptymalizowane przy użyciu obliczeń B3LYP/631g.
str_geometries = {
"1.51": "S -1.239044 0.671232 -0.030374; Li -1.506327 0.432403 -1.498949; Li -0.899996 0.973348 1.826768",
"1.91": "S -1.215858 0.692272 0.099232; Li -1.553305 0.390283 -1.758043; Li -0.876205 0.994426 1.956257",
"2.40": "S -1.741432 0.680397 0.346702; Li -0.529307 0.488006 -1.729343; Li -1.284307 0.989409 2.177209",
"3.10": "S -2.347450 0.657089 0.566194; Li -0.199353 0.527517 -1.665148; Li -1.008243 0.973206 1.893522",
"3.80": "S -2.707255 0.674298 0.909161; Li 0.079218 0.552012 -1.671656; Li -0.927010 0.931502 1.557063",
"4.50": "S -2.913363 0.709175 1.276987; Li 0.368656 0.559989 -1.798088; Li -1.010340 0.888647 1.315670",
}
str_geometries
{'1.51': 'S -1.239044 0.671232 -0.030374; Li -1.506327 0.432403 -1.498949; Li -0.899996 0.973348 1.826768',
'1.91': 'S -1.215858 0.692272 0.099232; Li -1.553305 0.390283 -1.758043; Li -0.876205 0.994426 1.956257',
'2.40': 'S -1.741432 0.680397 0.346702; Li -0.529307 0.488006 -1.729343; Li -1.284307 0.989409 2.177209',
'3.10': 'S -2.347450 0.657089 0.566194; Li -0.199353 0.527517 -1.665148; Li -1.008243 0.973206 1.893522',
'3.80': 'S -2.707255 0.674298 0.909161; Li 0.079218 0.552012 -1.671656; Li -0.927010 0.931502 1.557063',
'4.50': 'S -2.913363 0.709175 1.276987; Li 0.368656 0.559989 -1.798088; Li -1.010340 0.888647 1.315670'}
Obliczenia HiVQE zostaną wykonane z opcjami zdefiniowanymi poniżej. Używając bazy sto3g dla , mamy 19 orbitali przestrzennych z 22 elektronami. Aby uruchomić przypadek (10o,10e) z obliczeniami HiVQE, możesz zdefiniować 10 aktywnych orbitali i sześć zamrożonych orbitali. W każdej iteracji 100 strzałów zostanie użytych do próbkowania konfiguracji elektronowej generowanej przez obwód kwantowy ExcitationPreserving (epa) z splataniem circular i dwoma powtórzeniami (reps). Maksymalna liczba iteracji wynosi 30, aby zapewnić zakończenie iteracji po osiągnięciu zbieżności energii.
molecule_options = {
"basis": "sto3g",
"active_orbitals": list(range(5, 15)),
"frozen_orbitals": list(range(5)),
}
hivqe_options = {
"shots": 100,
"max_iter": 30,
"ansatz": "epa",
"ansatz_entanglement": "circular",
"ansatz_reps": 2,
}
Kroki 2 i 3: Optymalizacja problemu do wykonania na sprzęcie kwantowym i wykonanie za pomocą funkcji HiVQE Chemistry
Skonfiguruj pętlę for, aby uruchomić obliczenia HiVQE z geometriami przy użyciu opcji zdefiniowanych poniżej. Zadania są przesyłane w pętli for. W tym samouczku prześlesz sześć geometrii i pobierzesz wyniki po ich wszystkich ukończeniu. W głównym uruchomieniu funkcji musisz zdefiniować max_states i max_expansion_states, aby kontrolować maksymalny rozmiar macierzy podprzestrzeni oraz liczbę stanów, które mogą być generowane przy użyciu klasycznych metod rozszerzania CI na iterację. Identyfikatory zadań funkcji zostaną zapisane w słowniku z etykietą każdej geometrii, aby umożliwić dalsze śledzenie i przetwarzanie wyników.
info_jobid = {}
for dis, geom in str_geometries.items():
hivqe_run = hivqe.run(
geometry=geom,
backend_name="",
max_states=40000,
max_expansion_states=100,
molecule_options=molecule_options,
hivqe_options=hivqe_options,
)
status = hivqe_run.status()
info_jobid[dis] = hivqe_run.job_id
print(info_jobid)
{'1.51': 'de3b8818-c9db-4fa3-a3c2-d51551c2dfaf', '1.91': '55d9467a-fc85-49a8-9bc6-8f6990e421e5', '2.40': '415112b3-69ff-4d53-8b10-cb4e3be68c9e', '3.10': 'ef67b600-3887-4225-b872-e354dfdf8454', '3.80': 'b16d3502-a9e4-4560-9775-852e9d07e70f', '4.50': '0c0bffc7-af77-4a56-a656-2a2610c991d6'}
Sprawdźmy, czy wszystkie zadania nadal się wykonują, czy zostały ukończone.
completed_jobs_num = 0
running_jobs_num = 0
completed_jobs = {}
for i, info in enumerate(info_jobid.items()):
dis, job_id = info
submitted_job = catalog.get_job_by_id(job_id)
stat = submitted_job.status()
print(dis, submitted_job.job_id, stat)
if stat == "DONE":
completed_jobs_num += 1
completed_jobs[dis] = submitted_job
if (stat == "RUNNING") or (stat == "QUEUED"):
running_jobs_num += 1
print(
f"Completed {completed_jobs_num} job, Running or Queued {running_jobs_num} job"
)
1.51 de3b8818-c9db-4fa3-a3c2-d51551c2dfaf DONE
1.91 55d9467a-fc85-49a8-9bc6-8f6990e421e5 DONE
2.40 415112b3-69ff-4d53-8b10-cb4e3be68c9e DONE
3.10 ef67b600-3887-4225-b872-e354dfdf8454 DONE
3.80 b16d3502-a9e4-4560-9775-852e9d07e70f DONE
4.50 0c0bffc7-af77-4a56-a656-2a2610c991d6 DONE
Completed 6 job, Running or Queued 0 job
Po ukończeniu wszystkich zadań pobierzmy wszystkie wyniki obliczeń.
hivqe_result = {}
if len(info_jobid) == completed_jobs_num:
print("All jobs are completed")
for i, job in enumerate(completed_jobs.items()):
dis, cal = job
print(dis, cal.result()["energy"])
hivqe_result[str(dis)] = cal.result()["energy"]
All jobs are completed
1.51 -407.8944801731773
1.91 -407.9800570932916
2.40 -407.9372992999806
3.10 -407.86278336000134
3.80 -407.83092972296157
4.50 -407.82971011225766
pprint.pprint(hivqe_result)
{'1.51': -407.8944801731773,
'1.91': -407.9800570932916,
'2.40': -407.9372992999806,
'3.10': -407.86278336000134,
'3.80': -407.83092972296157,
'4.50': -407.82971011225766}
Całkowity czas QPU wykorzystany w zadaniu można śledzić, logując się do IBM Quantum Platform i przeglądając przesłane zadania z tagiem qunova-chemistry-hivqe.
Krok 4: Przetwarzanie końcowe i porównanie z metodami klasycznymi
Klasyczne obliczenia referencyjne (CASCI) można przeprowadzić dla przypadku (10o,10e), aby zweryfikować wyniki HiVQE.
str_geometries = {
"1.31": "S -1.250686 0.660708 -0.095168; Li -1.482812 0.453464 -1.369406; Li -0.911870 0.962810 1.762020",
"1.41": "S -1.244856 0.665971 -0.062773; Li -1.494574 0.442933 -1.434177; Li -0.905937 0.968078 1.794395",
"1.51": "S -1.239044 0.671232 -0.030374; Li -1.506327 0.432403 -1.498949; Li -0.899996 0.973348 1.826768",
"1.61": "S -1.233245 0.676492 0.002027; Li -1.518073 0.421873 -1.563722; Li -0.894049 0.978617 1.859141",
"1.71": "S -1.227453 0.681752 0.034429; Li -1.529816 0.411343 -1.628496; Li -0.888099 0.983887 1.891513",
"1.81": "S -1.221659 0.687012 0.066831; Li -1.541558 0.400813 -1.693270; Li -0.882150 0.989157 1.923885",
"1.91": "S -1.215858 0.692272 0.099232; Li -1.553305 0.390283 -1.758043; Li -0.876205 0.994426 1.956257",
"2.01": "S -1.209887 0.697544 0.131599; Li -1.565136 0.379748 -1.822800; Li -0.870344 0.999691 1.988646",
"2.11": "S -1.203945 0.702813 0.163973; Li -1.576953 0.369214 -1.887560; Li -0.864469 1.004956 2.021033",
"2.21": "S -1.198023 0.708081 0.196350; Li -1.588760 0.358680 -1.952322; Li -0.858584 1.010221 2.053417",
"2.30": "S -1.365426 0.717714 0.367060; Li -0.689401 0.458925 -1.828368; Li -1.500219 0.981173 2.255876",
"2.31": "S -1.192118 0.713348 0.228731; Li -1.600559 0.348146 -2.017085; Li -0.852690 1.015488 2.085800",
"2.40": "S -1.741432 0.680397 0.346702; Li -0.529307 0.488006 -1.729343; Li -1.284307 0.989409 2.177209",
"2.50": "S -1.885961 0.669986 0.365815; Li -0.461563 0.499084 -1.695846; Li -1.207523 0.988741 2.124599",
"2.60": "S -1.977163 0.665155 0.389784; Li -0.416654 0.504966 -1.683655; Li -1.161229 0.987690 2.088439",
"2.70": "S -2.063642 0.661518 0.418977; Li -0.367600 0.510505 -1.676408; Li -1.123804 0.985788 2.051998",
"2.80": "S -2.141072 0.659218 0.451663; Li -0.323153 0.515056 -1.673046; Li -1.090821 0.983538 2.015951",
"2.90": "S -2.212097 0.657968 0.487535; Li -0.281989 0.518909 -1.672407; Li -1.060960 0.980935 1.979440",
"3.00": "S -2.281477 0.657123 0.525155; Li -0.239607 0.523326 -1.668669; Li -1.033963 0.977363 1.938081",
"3.10": "S -2.347450 0.657089 0.566194; Li -0.199353 0.527517 -1.665148; Li -1.008243 0.973206 1.893522",
"3.20": "S -2.410882 0.657532 0.608912; Li -0.157788 0.532069 -1.659971; Li -0.986376 0.968211 1.845627",
"3.30": "S -2.470306 0.658818 0.654893; Li -0.118007 0.536237 -1.656311; Li -0.966733 0.962757 1.795986",
"3.40": "S -2.525776 0.660762 0.702910; Li -0.078312 0.540189 -1.654076; Li -0.950958 0.956861 1.745734",
"3.50": "S -2.576885 0.663376 0.752788; Li -0.039076 0.543706 -1.654536; Li -0.939085 0.950730 1.696316",
"3.60": "S -2.623930 0.666534 0.803853; Li 0.000274 0.546839 -1.657697; Li -0.931390 0.944439 1.648412",
"3.70": "S -2.667364 0.670217 0.856250; Li 0.039572 0.549616 -1.663265; Li -0.927254 0.937980 1.601583",
"3.80": "S -2.707255 0.674298 0.909161; Li 0.079218 0.552012 -1.671656; Li -0.927010 0.931502 1.557063",
"3.90": "S -2.744005 0.678718 0.962425; Li 0.119268 0.554073 -1.682595; Li -0.930310 0.925021 1.514738",
"4.00": "S -2.777891 0.683415 1.015798; Li 0.159751 0.555810 -1.696024; Li -0.936907 0.918587 1.474794",
"4.10": "S -2.809179 0.688333 1.069057; Li 0.200678 0.557234 -1.711873; Li -0.946546 0.912245 1.437385",
"4.20": "S -2.838194 0.693443 1.122205; Li 0.242066 0.558401 -1.729770; Li -0.958918 0.905968 1.402134",
"4.30": "S -2.864984 0.698619 1.174415; Li 0.283858 0.559186 -1.750539; Li -0.973920 0.900007 1.370693",
"4.40": "S -2.889984 0.703887 1.226140; Li 0.326068 0.559728 -1.773231; Li -0.991131 0.894196 1.341660",
"4.50": "S -2.913363 0.709175 1.276987; Li 0.368656 0.559989 -1.798088; Li -1.010340 0.888647 1.315670",
}
rhf_result = {}
casci_result = {}
cas_list = molecule_options["active_orbitals"]
distance_ref = []
for dis, geom in str_geometries.items():
distance_ref.append(dis)
mole = gto.M(atom=geom, basis=molecule_options["basis"])
mole.verbose = 0
# RHF energy
mf = scf.RHF(mole).run()
mo_occ = mf.mo_occ
num_elecs_as = int(sum([mo_occ[idx] for idx in cas_list]))
rhf_result[str(dis)] = mf.e_tot
# CASCI energy
casci_solver = mcscf.CASCI(mf, len(cas_list), num_elecs_as)
orbs = mcscf.addons.sort_mo(casci_solver, mf.mo_coeff, cas_list, base=0)
casci_solver.kernel(orbs)
casci_result[str(dis)] = casci_solver.e_tot
print(
f"d={dis:4.3} RHF Energy: {mf.e_tot:14.10}, CASCI Energy: {casci_solver.e_tot:14.10}"
)
d=1.3 RHF Energy: -407.7137006, CASCI Energy: -407.7193917
d=1.4 RHF Energy: -407.8183196, CASCI Energy: -407.8245211
d=1.5 RHF Energy: -407.8878013, CASCI Energy: -407.8944802
d=1.6 RHF Energy: -407.9315356, CASCI Energy: -407.9385663
d=1.7 RHF Energy: -407.9569034, CASCI Energy: -407.9641258
d=1.8 RHF Energy: -407.9693681, CASCI Energy: -407.9766313
d=1.9 RHF Energy: -407.9728592, CASCI Energy: -407.9800572
d=2.0 RHF Energy: -407.9701684, CASCI Energy: -407.9772549
d=2.1 RHF Energy: -407.9632701, CASCI Energy: -407.9702381
d=2.2 RHF Energy: -407.9535584, CASCI Energy: -407.9604007
d=2.3 RHF Energy: -407.9420173, CASCI Energy: -407.9487043
d=2.3 RHF Energy: -407.9420156, CASCI Energy: -407.9487024
d=2.4 RHF Energy: -407.9297216, CASCI Energy: -407.9372993
d=2.5 RHF Energy: -407.9172, CASCI Energy: -407.9261859
d=2.6 RHF Energy: -407.9061139, CASCI Energy: -407.915961
d=2.7 RHF Energy: -407.8937118, CASCI Energy: -407.904259
d=2.8 RHF Energy: -407.8816389, CASCI Energy: -407.8928292
d=2.9 RHF Energy: -407.8700448, CASCI Energy: -407.8819574
d=3.0 RHF Energy: -407.859054, CASCI Energy: -407.8719092
d=3.1 RHF Energy: -407.8487619, CASCI Energy: -407.8628304
d=3.2 RHF Energy: -407.8392304, CASCI Energy: -407.8548482
d=3.3 RHF Energy: -407.8304842, CASCI Energy: -407.8480217
d=3.4 RHF Energy: -407.8225124, CASCI Energy: -407.8423743
d=3.5 RHF Energy: -407.8152758, CASCI Energy: -407.8378892
d=3.6 RHF Energy: -407.8087161, CASCI Energy: -407.8345331
d=3.7 RHF Energy: -407.802764, CASCI Energy: -407.8322563
d=3.8 RHF Energy: -407.7973458, CASCI Energy: -407.83093
d=3.9 RHF Energy: -407.7923883, CASCI Energy: -407.8303555
d=4.0 RHF Energy: -407.7878216, CASCI Energy: -407.83025
d=4.1 RHF Energy: -407.783582, CASCI Energy: -407.8303243
d=4.2 RHF Energy: -407.7796124, CASCI Energy: -407.8303791
d=4.3 RHF Energy: -407.7758633, CASCI Energy: -407.8302885
d=4.4 RHF Energy: -407.7722923, CASCI Energy: -407.8300614
d=4.5 RHF Energy: -407.7688641, CASCI Energy: -407.829711
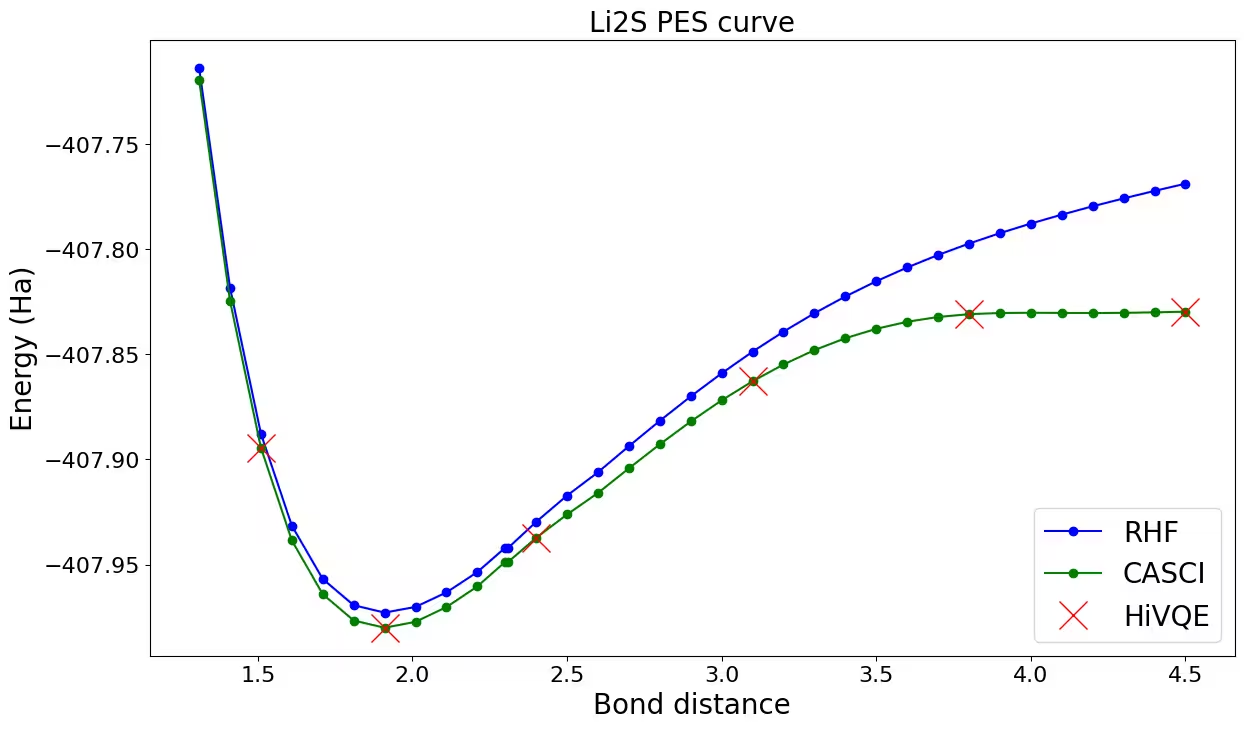
Wykres krzywej dysocjacji dla Li_2S
Narysujmy wykres i porównajmy wyniki HiVQE z HF i CASCI. Możesz zaobserwować, że wszystkie obliczenia HiVQE dobrze zgadzają się z klasycznym wynikiem referencyjnym (CASCI).
fig, ax = plt.subplots(1, 1)
hf_energy = [v for key, v in rhf_result.items()]
casci_energy = [v for key, v in casci_result.items()]
hivqe_energy = [v for key, v in hivqe_result.items()]
distance_ref = [float(key) for key, v in rhf_result.items()]
distance = [float(key) for key, v in hivqe_result.items()]
ax.plot(distance_ref, hf_energy, "-o", label="RHF", c="blue")
ax.plot(distance_ref, casci_energy, "-o", label="CASCI", c="green")
ax.plot(distance, hivqe_energy, "x", label="HiVQE", c="red", markersize=20)
ax.legend(fontsize=20)
ax.tick_params("both", labelsize=16)
ax.set_xlabel("Bond distance (angstrom)", size=20)
ax.set_ylabel("Energy (Ha)", size=20)
ax.set_title("Li2S PES curve", size=20)
fig.set_size_inches(14, 8)
Część 2: FeP-NO (44Q)
Krok 1: Odwzorowanie klasycznych danych wejściowych na problem kwantowy
Zdefiniuj opcje dla obliczeń HiVQE.
molecule_options = {
"basis": "631g*",
"active_orbitals": list(range(90, 112, 1)),
"frozen_orbitals": list(range(0, 90, 1)),
"charge": -1,
}
hivqe_options = {
"shots": 2000,
"max_iter": 40,
"ansatz": "epa",
"ansatz_entanglement": "linear",
"ansatz_reps": 2,
"amplitude_screening_tolerance": 1e-6,
}
Zdefiniuj geometrie FeP-NO w formacie słownika dla różnych odległości wiązania Fe-N, aby obliczyć krzywą PES.
geometry_1_75 = """
Fe 9.910596 31.534095 1.798088
N 10.557481 31.888419 -0.055204
N 11.823496 31.255002 2.384659
N 9.292831 30.783362 3.568730
N 8.036805 31.418327 1.124265
C 9.784765 32.177349 -1.158798
C 10.612656 32.501029 -2.296868
C 11.903375 32.404043 -1.876832
C 11.859093 32.028943 -0.483750
C 12.965737 31.464698 1.641427
C 14.146517 31.236323 2.440231
C 13.713061 30.885870 3.681911
C 12.268752 30.896411 3.634891
C 10.067717 30.486167 4.664747
C 9.246224 30.053411 5.772052
C 7.957075 30.082846 5.336488
C 7.995710 30.538421 3.967046
C 6.900258 31.104497 1.836595
C 5.722470 31.251707 1.015333
C 6.148430 31.668586 -0.207993
C 7.587039 31.767438 -0.130483
C 8.399453 32.134197 -1.192329
H 7.912872 32.388031 -2.131079
C 12.984883 31.836053 0.306093
H 13.955948 31.977044 -0.162626
C 11.453768 30.560663 4.708020
H 11.940677 30.298823 5.644352
C 6.877071 30.697580 3.164102
H 5.907240 30.476797 3.603674
H 12.813946 32.569160 -2.441577
H 10.236332 32.758110 -3.280309
H 15.164312 31.335191 2.080201
H 14.299625 30.629109 4.556760
H 9.626524 29.758225 6.743433
H 7.053076 29.823583 5.875809
H 4.709768 31.058315 1.350561
H 5.561898 31.886355 -1.093106
N 9.832739 33.209042 2.298783
O 9.346337 34.075996 1.606023
"""
geometry_2_00 = """
Fe 9.917990 31.445558 1.778346
N 10.556809 31.866188 -0.055498
N 11.814089 31.227003 2.372666
N 9.297875 30.758246 3.550104
N 8.043584 31.397768 1.120485
C 9.784831 32.164652 -1.160219
C 10.611624 32.501801 -2.293514
C 11.902858 32.406547 -1.875160
C 11.859552 32.017818 -0.486307
C 12.960503 31.454432 1.636717
C 14.140770 31.242960 2.439615
C 13.708543 30.884151 3.678983
C 12.266351 30.874173 3.627468
C 10.070264 30.465070 4.655102
C 9.247247 30.053101 5.766681
C 7.958085 30.091201 5.332866
C 7.998432 30.529979 3.958727
C 6.901428 31.093932 1.833807
C 5.723289 31.255057 1.016540
C 6.151314 31.670649 -0.206350
C 7.589736 31.755538 -0.133074
C 8.400230 32.124963 -1.194447
H 7.913264 32.386655 -2.130914
C 12.983905 31.827747 0.302415
H 13.955696 31.979687 -0.161365
C 11.454251 30.533644 4.698234
H 11.941002 30.276716 5.636156
C 6.877444 30.689985 3.159940
H 5.907605 30.480118 3.604825
H 12.813105 32.581608 -2.437367
H 10.233725 32.768337 -3.273979
H 15.157796 31.357524 2.082132
H 14.295001 30.638320 4.557047
H 9.626721 29.768762 6.741623
H 7.051752 29.847502 5.875478
H 4.709710 31.071712 1.354640
H 5.565103 31.898376 -1.089333
N 9.840508 33.353531 2.373019
O 9.344561 34.158205 1.637232
"""
geometry_5_00 = """
Fe 9.918629 31.289202 1.717339
N 10.542914 31.832173 -0.080685
N 11.795572 31.199413 2.341831
N 9.294593 30.741247 3.513929
N 8.042689 31.359481 1.087282
C 9.775254 32.111817 -1.200449
C 10.600219 32.479101 -2.319680
C 11.891090 32.425876 -1.887580
C 11.847694 32.024341 -0.507342
C 12.945734 31.464689 1.611366
C 14.116395 31.289997 2.423572
C 13.685777 30.915122 3.663719
C 12.252381 30.861042 3.608186
C 10.062170 30.463021 4.634102
C 9.236749 30.104333 5.755782
C 7.945687 30.161198 5.324720
C 7.989641 30.552269 3.941498
C 6.892881 31.087489 1.815829
C 5.722676 31.253502 1.001149
C 6.153153 31.631057 -0.238233
C 7.586010 31.695401 -0.179773
C 8.390724 32.047572 -1.247553
H 7.903308 32.291586 -2.187969
C 12.973334 31.849872 0.283741
H 13.944682 32.031190 -0.169145
C 11.447158 30.518591 4.678739
H 11.934423 30.277429 5.619969
C 6.864795 30.711643 3.146118
H 5.893357 30.532078 3.599511
H 12.800139 32.636412 -2.439296
H 10.224017 32.743662 -3.301293
H 15.131785 31.441247 2.076257
H 14.273933 30.694315 4.546802
H 9.612512 29.848040 6.739754
H 7.036117 29.960530 5.879248
H 4.707408 31.099933 1.347803
H 5.564992 31.851940 -1.121294
N 9.666041 36.091609 3.085945
O 9.598728 37.226756 3.411299
"""
str_geometries = {
"1.75": geometry_1_75,
"2.00": geometry_2_00,
"5.00": geometry_5_00,
}
hivqe_result = {}
{'5.0': '\nFe 9.918629 31.289202 1.717339\nN 10.542914 31.832173 -0.080685\nN 11.795572 31.199413 2.341831\nN 9.294593 30.741247 3.513929\nN 8.042689 31.359481 1.087282\nC 9.775254 32.111817 -1.200449\nC 10.600219 32.479101 -2.319680\nC 11.891090 32.425876 -1.887580\nC 11.847694 32.024341 -0.507342\nC 12.945734 31.464689 1.611366\nC 14.116395 31.289997 2.423572\nC 13.685777 30.915122 3.663719\nC 12.252381 30.861042 3.608186\nC 10.062170 30.463021 4.634102\nC 9.236749 30.104333 5.755782\nC 7.945687 30.161198 5.324720\nC 7.989641 30.552269 3.941498\nC 6.892881 31.087489 1.815829\nC 5.722676 31.253502 1.001149\nC 6.153153 31.631057 -0.238233\nC 7.586010 31.695401 -0.179773\nC 8.390724 32.047572 -1.247553\nH 7.903308 32.291586 -2.187969\nC 12.973334 31.849872 0.283741\nH 13.944682 32.031190 -0.169145\nC 11.447158 30.518591 4.678739\nH 11.934423 30.277429 5.619969\nC 6.864795 30.711643 3.146118\nH 5.893357 30.532078 3.599511\nH 12.800139 32.636412 -2.439296\nH 10.224017 32.743662 -3.301293\nH 15.131785 31.441247 2.076257\nH 14.273933 30.694315 4.546802\nH 9.612512 29.848040 6.739754\nH 7.036117 29.960530 5.879248\nH 4.707408 31.099933 1.347803\nH 5.564992 31.851940 -1.121294\nN 9.666041 36.091609 3.085945\nO 9.598728 37.226756 3.411299\n'}
geometry_1_75 = """
Fe 9.910596 31.534095 1.798088
N 10.557481 31.888419 -0.055204
N 11.823496 31.255002 2.384659
N 9.292831 30.783362 3.568730
N 8.036805 31.418327 1.124265
C 9.784765 32.177349 -1.158798
C 10.612656 32.501029 -2.296868
C 11.903375 32.404043 -1.876832
C 11.859093 32.028943 -0.483750
C 12.965737 31.464698 1.641427
C 14.146517 31.236323 2.440231
C 13.713061 30.885870 3.681911
C 12.268752 30.896411 3.634891
C 10.067717 30.486167 4.664747
C 9.246224 30.053411 5.772052
C 7.957075 30.082846 5.336488
C 7.995710 30.538421 3.967046
C 6.900258 31.104497 1.836595
C 5.722470 31.251707 1.015333
C 6.148430 31.668586 -0.207993
C 7.587039 31.767438 -0.130483
C 8.399453 32.134197 -1.192329
H 7.912872 32.388031 -2.131079
C 12.984883 31.836053 0.306093
H 13.955948 31.977044 -0.162626
C 11.453768 30.560663 4.708020
H 11.940677 30.298823 5.644352
C 6.877071 30.697580 3.164102
H 5.907240 30.476797 3.603674
H 12.813946 32.569160 -2.441577
H 10.236332 32.758110 -3.280309
H 15.164312 31.335191 2.080201
H 14.299625 30.629109 4.556760
H 9.626524 29.758225 6.743433
H 7.053076 29.823583 5.875809
H 4.709768 31.058315 1.350561
H 5.561898 31.886355 -1.093106
N 9.832739 33.209042 2.298783
O 9.346337 34.075996 1.606023
"""
geometry_2_00 = """
Fe 9.917990 31.445558 1.778346
N 10.556809 31.866188 -0.055498
N 11.814089 31.227003 2.372666
N 9.297875 30.758246 3.550104
N 8.043584 31.397768 1.120485
C 9.784831 32.164652 -1.160219
C 10.611624 32.501801 -2.293514
C 11.902858 32.406547 -1.875160
C 11.859552 32.017818 -0.486307
C 12.960503 31.454432 1.636717
C 14.140770 31.242960 2.439615
C 13.708543 30.884151 3.678983
C 12.266351 30.874173 3.627468
C 10.070264 30.465070 4.655102
C 9.247247 30.053101 5.766681
C 7.958085 30.091201 5.332866
C 7.998432 30.529979 3.958727
C 6.901428 31.093932 1.833807
C 5.723289 31.255057 1.016540
C 6.151314 31.670649 -0.206350
C 7.589736 31.755538 -0.133074
C 8.400230 32.124963 -1.194447
H 7.913264 32.386655 -2.130914
C 12.983905 31.827747 0.302415
H 13.955696 31.979687 -0.161365
C 11.454251 30.533644 4.698234
H 11.941002 30.276716 5.636156
C 6.877444 30.689985 3.159940
H 5.907605 30.480118 3.604825
H 12.813105 32.581608 -2.437367
H 10.233725 32.768337 -3.273979
H 15.157796 31.357524 2.082132
H 14.295001 30.638320 4.557047
H 9.626721 29.768762 6.741623
H 7.051752 29.847502 5.875478
H 4.709710 31.071712 1.354640
H 5.565103 31.898376 -1.089333
N 9.840508 33.353531 2.373019
O 9.344561 34.158205 1.637232
"""
geometry_5_00 = """
Fe 9.918629 31.289202 1.717339
N 10.542914 31.832173 -0.080685
N 11.795572 31.199413 2.341831
N 9.294593 30.741247 3.513929
N 8.042689 31.359481 1.087282
C 9.775254 32.111817 -1.200449
C 10.600219 32.479101 -2.319680
C 11.891090 32.425876 -1.887580
C 11.847694 32.024341 -0.507342
C 12.945734 31.464689 1.611366
C 14.116395 31.289997 2.423572
C 13.685777 30.915122 3.663719
C 12.252381 30.861042 3.608186
C 10.062170 30.463021 4.634102
C 9.236749 30.104333 5.755782
C 7.945687 30.161198 5.324720
C 7.989641 30.552269 3.941498
C 6.892881 31.087489 1.815829
C 5.722676 31.253502 1.001149
C 6.153153 31.631057 -0.238233
C 7.586010 31.695401 -0.179773
C 8.390724 32.047572 -1.247553
H 7.903308 32.291586 -2.187969
C 12.973334 31.849872 0.283741
H 13.944682 32.031190 -0.169145
C 11.447158 30.518591 4.678739
H 11.934423 30.277429 5.619969
C 6.864795 30.711643 3.146118
H 5.893357 30.532078 3.599511
H 12.800139 32.636412 -2.439296
H 10.224017 32.743662 -3.301293
H 15.131785 31.441247 2.076257
H 14.273933 30.694315 4.546802
H 9.612512 29.848040 6.739754
H 7.036117 29.960530 5.879248
H 4.707408 31.099933 1.347803
H 5.564992 31.851940 -1.121294
N 9.666041 36.091609 3.085945
O 9.598728 37.226756 3.411299
"""
str_geometries = {
"1.75": geometry_1_75,
"2.00": geometry_2_00,
"5.00": geometry_5_00,
}
hivqe_result = {}
{'5.0': '\nFe 9.918629 31.289202 1.717339\nN 10.542914 31.832173 -0.080685\nN 11.795572 31.199413 2.341831\nN 9.294593 30.741247 3.513929\nN 8.042689 31.359481 1.087282\nC 9.775254 32.111817 -1.200449\nC 10.600219 32.479101 -2.319680\nC 11.891090 32.425876 -1.887580\nC 11.847694 32.024341 -0.507342\nC 12.945734 31.464689 1.611366\nC 14.116395 31.289997 2.423572\nC 13.685777 30.915122 3.663719\nC 12.252381 30.861042 3.608186\nC 10.062170 30.463021 4.634102\nC 9.236749 30.104333 5.755782\nC 7.945687 30.161198 5.324720\nC 7.989641 30.552269 3.941498\nC 6.892881 31.087489 1.815829\nC 5.722676 31.253502 1.001149\nC 6.153153 31.631057 -0.238233\nC 7.586010 31.695401 -0.179773\nC 8.390724 32.047572 -1.247553\nH 7.903308 32.291586 -2.187969\nC 12.973334 31.849872 0.283741\nH 13.944682 32.031190 -0.169145\nC 11.447158 30.518591 4.678739\nH 11.934423 30.277429 5.619969\nC 6.864795 30.711643 3.146118\nH 5.893357 30.532078 3.599511\nH 12.800139 32.636412 -2.439296\nH 10.224017 32.743662 -3.301293\nH 15.131785 31.441247 2.076257\nH 14.273933 30.694315 4.546802\nH 9.612512 29.848040 6.739754\nH 7.036117 29.960530 5.879248\nH 4.707408 31.099933 1.347803\nH 5.564992 31.851940 -1.121294\nN 9.666041 36.091609 3.085945\nO 9.598728 37.226756 3.411299\n'}
Kroki 2 i 3: Optymalizacja problemu pod kątem wykonania na sprzęcie kwantowym i uruchomienie za pomocą funkcji HiVQE Chemistry
Na podstawie konfiguracji HiVQE i geometrii uzyskaj wyniki sekwencyjnie.
Prześlij obliczenia dla d(Fe-N) = 1.75 .
hivqe_run_1_75 = hivqe.run(
geometry=str_geometries["1.75"],
backend_name="",
max_states=400000000,
max_expansion_states=100,
molecule_options=molecule_options,
hivqe_options=hivqe_options,
)
info_jobid_1_75 = hivqe_run_1_75.job_id
Śledź zadanie i pobierz wynik dla obliczeń d(Fe-N) = 1.75 .
submitted_job_1_75 = catalog.get_job_by_id(info_jobid_1_75)
stat = submitted_job_1_75.status()
print(submitted_job_1_75.job_id, stat)
if stat == "DONE":
hivqe_run_1_75_energy = submitted_job_1_75.result()["energy"]
print(f"Completed HiVQE calculation, Energy {hivqe_run_1_75_energy}")
hivqe_result["1.75"] = hivqe_run_1_75_energy
Prześlij obliczenia dla d(Fe-N) = 2.00 .
hivqe_run_2_00 = hivqe.run(
geometry=str_geometries["2.00"],
backend_name="",
max_states=400000000,
max_expansion_states=100,
molecule_options=molecule_options,
hivqe_options=hivqe_options,
)
info_jobid_2_00 = hivqe_run_2_00.job_id
Śledź zadanie i pobierz wynik dla obliczeń d(Fe-N) = 2.00 .
submitted_job_2_00 = catalog.get_job_by_id(info_jobid_2_00)
stat = submitted_job_2_00.status()
print(submitted_job_2_00.job_id, stat)
if stat == "DONE":
hivqe_run_2_00_energy = submitted_job_2_00.result()["energy"]
print(f"Completed HiVQE calculation, Energy {hivqe_run_2_00_energy}")
hivqe_result["2.00"] = hivqe_run_2_00_energy
Prześlij obliczenia dla d(Fe-N) = 5.00 .
hivqe_run_5_00 = hivqe.run(
geometry=str_geometries["5.00"],
backend_name="",
max_states=400000000,
max_expansion_states=100,
molecule_options=molecule_options,
hivqe_options=hivqe_options,
)
info_jobid_5_00 = hivqe_run_5_00.job_id
Śledź zadanie i pobierz wynik dla obliczeń d(Fe-N) = 5.00 .
submitted_job_5_00 = catalog.get_job_by_id(info_jobid_5_00)
stat = submitted_job_5_00.status()
print(submitted_job_5_00.job_id, stat)
if stat == "DONE":
hivqe_run_5_00_energy = submitted_job_5_00.result()["energy"]
print(f"Completed HiVQE calculation, Energy {hivqe_run_5_00_energy}")
hivqe_result["5.00"] = hivqe_run_5_00_energy
hivqe_result = {
"1.75": -2373.681781,
"2.00": -2373.694128,
"5.00": -2373.637807,
}
Krok 4: Przetwarzanie końcowe i porównanie z metodami klasycznymi
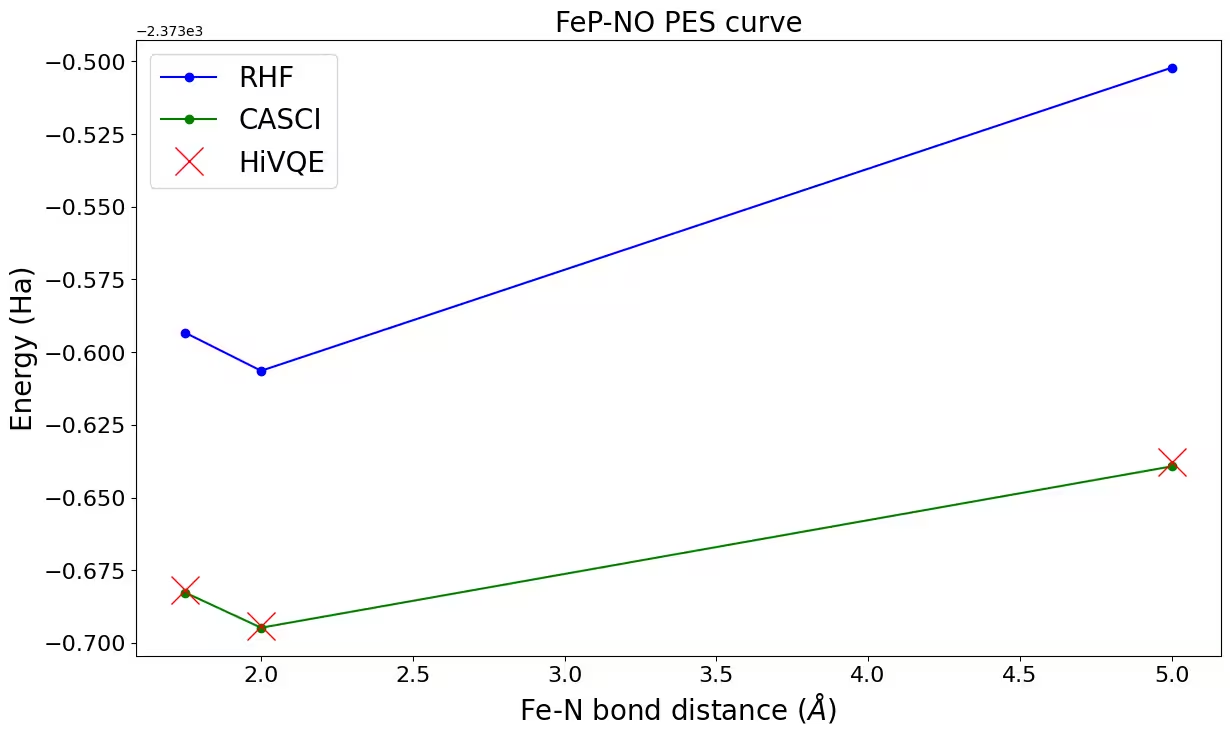
Klasyczne wyniki referencyjne (CASCI-DMRG, maxM=800) dla (22o,22e) są dostarczone w celu walidacji wyników HiVQE.
rhf_result = {
"1.75": -2373.59331683504,
"2.00": -2373.60640773065,
"5.00": -2373.50214278007,
}
casci_result = {"1.75": -2373.6827, "2.00": -2373.6948, "5.00": -2373.6393}
fig, ax = plt.subplots(1, 1)
hf_energy = [v for key, v in rhf_result.items()]
casci_energy = [v for key, v in casci_result.items()]
hivqe_energy = [v for key, v in hivqe_result.items()]
distance_ref = [float(key) for key, v in rhf_result.items()]
distance = [float(key) for key, v in hivqe_result.items()]
ax.plot(distance_ref, hf_energy, "-o", label="RHF", c="blue")
ax.plot(distance_ref, casci_energy, "-o", label="CASCI", c="green")
ax.plot(distance, hivqe_energy, "x", label="HiVQE", c="red", markersize=20)
ax.legend(fontsize=20)
ax.tick_params("both", labelsize=16)
ax.set_xlabel("Fe-N bond distance ($\AA$)", size=20)
ax.set_ylabel("Energy (Ha)", size=20)
ax.set_title("FeP-NO PES curve", size=20)
fig.set_size_inches(14, 8)
Ankieta dotycząca samouczka
Prosimy o wypełnienie krótkiej ankiety, aby przekazać nam opinię na temat tego samouczka. Twoje spostrzeżenia pomogą nam ulepszyć ofertę treści i doświadczenie użytkownika.
Note: This survey is provided by IBM Quantum and relates to the original English content. To give feedback on doQumentation's website, translations, or code execution, please open a GitHub issue.